VILLI INTESTINALI CON BATTERI
Misurazione dei Microbiomi
Storicamente l'identificazione dei microrganismi veniva condotta con metodi basati su colture. Questi metodi pongono notevoli limitazioni, tra cui l'impossibilità di sottoporre a coltura tutti gli organismi del microbioma.1-3
Non tutti i microrganismi sono vitali nelle condizioni in vitro associate ai metodi basati su colture.1
I metodi molecolari di nuova generazione utilizzano invece sequenze del DNA batterico come indicatori degli organismi per identificarne tassonomia, abbondanza relativa e funzione.1,4-6 Vengono brevemente descritti di seguito i metodi più comunemente utilizzati.
Panoramica dei metodi più comunemente utilizzati per la misurazione del microbioma
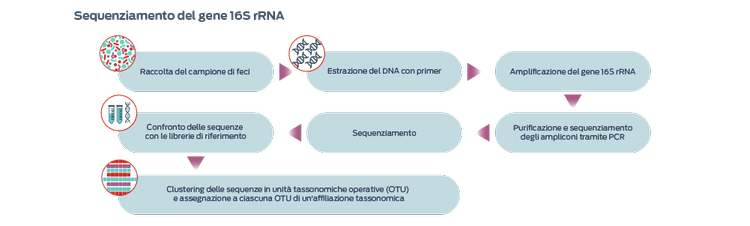
Sequenziamento di geni marcatori basato su ampliconi
L'approccio più comunemente utilizzato prevede il sequenziamento del gene codificante l'RNA ribosomiale (rRNA) 16S, presente in tutti i batteri e gli archei ma non nei funghi o nel regno animale, per generare un censimento microbico del campione.1,4,7 L'identificazione del micobioma sostituisce i geni 18S rRNA.7
Il gene 16S rRNA è altamente preservato in tutte le specie batteriche e include regioni ipervariabili che consentono la differenziazione.1 Questo approccio consente l'identificazione di molti microrganismi in un campione, compresi i microrganismi che non possono essere coltivati.1 Questa tecnica non permette tuttavia di distinguere tra microrganismi vivi o morti, transienti o residenti, commensali o patogeni, resistenti o sensibili agli antibiotici.1
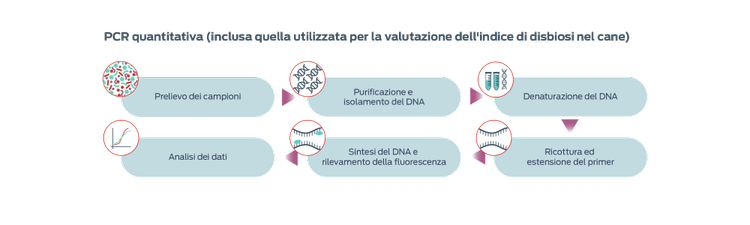
Reazione a catena della polimerasi (PCR) quantitativa
La PCR quantitativa è un metodo rapido e accessibile per quantificare specifici taxa batterici di interesse e consente lo sviluppo di intervalli di riferimento. Sulla base della PCR quantitativa relativa a sette specie batteriche, è stato sviluppato un indice della disbiosi del microbiota nel cane per tenere traccia delle variazioni del microbioma in risposta alla terapia.3
Collegamenti a un articolo in inglese non disponibile in italiano.
Descrizione del "censimento microbico"
Le unità tassonomiche operative (OTU) sono cluster di sequenze di DNA basati sulla somiglianza. Le sequenze rappresentative di ogni OTU vengono confrontate con i database di riferimento per assegnare l'identificazione dei microbi nel cluster.
Alfa diversità e beta diversità indicano la gamma di specie nel microbioma. La alfa diversità è una misura della diversità all'interno di un campione.1 La alfa diversità tiene conto della ricchezza (il numero di specie/OTU e la loro distribuzione) e dell'uniformità (l'abbondanza relativa dei diversi OTU/specie e della loro distribuzione). La alfa diversità si basa su algoritmi ed è comunemente espressa come indice, ad esempio l'indice di Shannon o l'indice di Simpson.1 La beta diversità è invece una misura della diversità tra campioni, spesso rappresentata come modelli di cluster. I sistemi utilizzati per calcolare la beta diversità includono Bray-Curtis e UniFrac ponderata e non ponderata.1
Dal censimento alla funzione
Con l'avanzare della ricerca, emergono due domande principali riguardo ai microbi: quali microbi sono presenti? Cosa stanno facendo? L'identificazione dei microrganismi presenti nel microbioma non fornisce informazioni sulla loro funzione.3,5 È probabile che alcune funzioni metaboliche e molecolari vengano assunte da più di un microbo, da cui deriverebbe un ecosistema ridondante in grado di offrire flessibilità e resilienza.3,8
A causa di questa ridondanza, l'analisi del microbioma basata sulle specie microbiche presenti nella popolazione è insufficiente per rilevare le variazioni funzionali nel microbioma. Sebbene l'abbondanza relativa dei microbi possa essere alterata o meno da un intervento o da una condizione, il microbioma presente potrebbe modificare le attività microbiche e il metabolismo per compensare; per poter rilevare tali variazioni, sono necessarie procedure analitiche diverse.
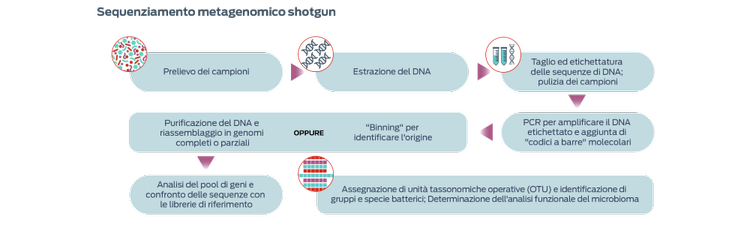
Sequenziamento metagenomico shotgun
I metodi shotgun, così definiti in quanto non mirati (ovvero non destinati a rilevare la presenza di una serie predeterminata di microbi), stanno acquisendo popolarità nell'analisi del microbioma degli animali. Questi metodi offrono il vantaggio di sequenziare geni funzionali, invece di individuare semplicemente l'identificazione batterica.3-5 Tali processi richiedono tuttavia quantità maggiori di DNA dai campioni e sono più costosi.3
Il sequenziamento a lettura lunga facilita l'assemblaggio di genomi completi, compresi i geni solitamente non rilevati con la metagenomica a lettura breve e che forniscono ulteriori informazioni biologiche.6
Metabolomica, proteomica e trascrittomica
Questi processi misurano l'attività funzionale in un microbioma.4 Gli approcci metabolomici vengono utilizzati per determinare i profili dei metaboliti, solitamente caratterizzati mediante processi quali risonanza magnetica nucleare, spettroscopia, spettroscopia di massa e cromatografia liquida.7 Questi approcci mirano a esaminare le vie regolate dai microbi, come la produzione di acidi grassi a catena corta, il metabolismo degli acidi biliari, la produzione di neutrotrasmettitori e la produzione di indolo.3

Scopri Altre Aree del Forum sul Microbioma

Interventi Incentrati sul Microbioma per le Condizioni di Salute Degli Animali Domestici
Ulteriori informazioni
- Belas, A., Marques, C., & Pomba, C. (2020). The gut microbiome and antimicrobial resistance in companion animals. In Duarte, A. & Lopes da Costa, L. (Eds.), Advances in Animal Health, Medicine and Production (1st ed.), pp. 233—245. Springer International Publishing
- Cunningham, M., Azcarate-Peril, M. A., Barnard, A., Benoit, V., Grimaldi, R., Guyonnet, D.,…Gibson, G. R. (2021). Shaping the future of probiotics and prebiotics. Trends in Microbiology, 29(8), 667—685. doi:10.1016/j.tim.2021.01.003
- Pilla, R., & Suchodolski, J. S. (2021). The gut microbiome of dogs and cats, and the influence of diet. Veterinary Clinics of North America Small Animal Practice, 51(3), 605–621. doi:10.1016/j.cvsm.2021.01.002
- Bokulich, N. A., Ziemski, M., Robeson, M. S., & Kaehler, B. D. (2020). Measuring the microbiome: Best practices for developing and benchmarking microbiomics methods. Computational and Structural Biotechnology Journal, 18, 4048–4062. doi:10.1016/j.csbj.2020.11.049
- Radjabzadeh, D., Uitterlinden, A. G., & Kraaij, R. (2017). Microbiome measurement: Possibilities and pitfalls. Best Practice & Research Clinical Gastroenterology, 31, 619–623. doi:10.1016/j.bpg.2017.10.008
- Cusco, A., Pérez, D., Viñes, J., Fàbregas, N., & Francino, O. (2020). Long-read metagenomics retrieve complete single-contig bacterial genomes from canine feces. In review, BMC Genomics. doi:10.21203/rs.3.rs-135952/v1
- Marchesi, J. R. & Ravel, J. (2015). The vocabulary of microbiome research: a proposal. Microbiome, 3, 31. doi:10.1186/s40168-015-0095-5
- Koidl, L., & Untersmayr, E. (2021). The clinical implications of the microbiome in the development of allergy diseases. Expert Review of Clinical Immunology, 17, 115—126. doi:10.1080/1744666X.2021.1874353
